KaroL3121-web
AD4: conexión con la API de la COVID19 y análisis con Pandas
Me conecto a la API https://api.covid19api.com/
import pandas as pd
Casos globales de la Covid19
Establezco una variable con el valor de la url.
url = 'https://api.covid19api.com/countries'
url
'https://api.covid19api.com/countries'
Creo el dataframe
Creamos un dataframe con la función de panda. Luego definimos el dataframe, la estructura de tablas/datos en Phyton y emplearemos la funcion de pd.read_json. Si lo llamo me sale el json en formato de tabla.
df = pd.read_json(url)
df
| Country | Slug | ISO2 | |
|---|---|---|---|
| 0 | Gibraltar | gibraltar | GI |
| 1 | Oman | oman | OM |
| 2 | France | france | FR |
| 3 | Jersey | jersey | JE |
| 4 | Mali | mali | ML |
| ... | ... | ... | ... |
| 243 | Puerto Rico | puerto-rico | PR |
| 244 | Papua New Guinea | papua-new-guinea | PG |
| 245 | Saint Pierre and Miquelon | saint-pierre-and-miquelon | PM |
| 246 | Timor-Leste | timor-leste | TL |
| 247 | Montenegro | montenegro | ME |
248 rows × 3 columns
Datos de la covid19 en España
Para que me salgan los datos de España creo una lista nueva donde le indico que el país que voy a seleccionar es == a Spain. Esto gracias a que tengo una lista que se llama Country.
df[df['Country'] == 'Spain']
| Country | Slug | ISO2 | |
|---|---|---|---|
| 141 | Spain | spain | ES |
Procedo a buscar los datos de España en tiempo real para lo que defino una url que se llama rt (de real time). También creo el objeto df_rt_es, el cual leerá la información de la url.
url_rt_es = 'https://api.covid19api.com/country/spain/status/confirmed/live'
df_rt_es = pd.read_json(url_rt_es)
df_rt_es
| Country | CountryCode | Province | City | CityCode | Lat | Lon | Cases | Status | Date | |
|---|---|---|---|---|---|---|---|---|---|---|
| 0 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-22 00:00:00+00:00 | |||
| 1 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-23 00:00:00+00:00 | |||
| 2 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-24 00:00:00+00:00 | |||
| 3 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-25 00:00:00+00:00 | |||
| 4 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-26 00:00:00+00:00 | |||
| ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... |
| 893 | Spain | ES | 40.46 | -3.75 | 12818184 | confirmed | 2022-07-03 00:00:00+00:00 | |||
| 894 | Spain | ES | 40.46 | -3.75 | 12818184 | confirmed | 2022-07-04 00:00:00+00:00 | |||
| 895 | Spain | ES | 40.46 | -3.75 | 12890002 | confirmed | 2022-07-05 00:00:00+00:00 | |||
| 896 | Spain | ES | 40.46 | -3.75 | 12890002 | confirmed | 2022-07-06 00:00:00+00:00 | |||
| 897 | Spain | ES | 40.46 | -3.75 | 12890002 | confirmed | 2022-07-07 00:00:00+00:00 |
898 rows × 10 columns
Casos de España de la parte superior de la tabla de datos
Esta visualización se logra colocando df_rt_es.head()
df_rt_es.head()
| Country | CountryCode | Province | City | CityCode | Lat | Lon | Cases | Status | Date | |
|---|---|---|---|---|---|---|---|---|---|---|
| 0 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-22 00:00:00+00:00 | |||
| 1 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-23 00:00:00+00:00 | |||
| 2 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-24 00:00:00+00:00 | |||
| 3 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-25 00:00:00+00:00 | |||
| 4 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-26 00:00:00+00:00 |
Casos de España de la parte inferior de la tabla de datos
Esta visualización se logra colocando df_rt_es.tail()
df_rt_es.tail()
| Country | CountryCode | Province | City | CityCode | Lat | Lon | Cases | Status | Date | |
|---|---|---|---|---|---|---|---|---|---|---|
| 893 | Spain | ES | 40.46 | -3.75 | 12818184 | confirmed | 2022-07-03 00:00:00+00:00 | |||
| 894 | Spain | ES | 40.46 | -3.75 | 12818184 | confirmed | 2022-07-04 00:00:00+00:00 | |||
| 895 | Spain | ES | 40.46 | -3.75 | 12890002 | confirmed | 2022-07-05 00:00:00+00:00 | |||
| 896 | Spain | ES | 40.46 | -3.75 | 12890002 | confirmed | 2022-07-06 00:00:00+00:00 | |||
| 897 | Spain | ES | 40.46 | -3.75 | 12890002 | confirmed | 2022-07-07 00:00:00+00:00 |
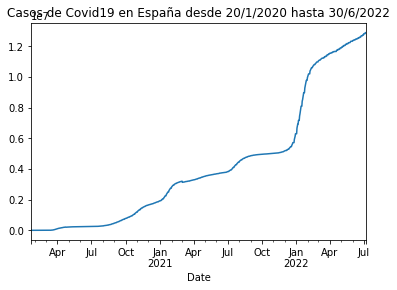
Visualización de los casos de covid-19 en España
Para visualizar los casos y fechas de España en una gráfica convierto a fecha en columna de control, estableciendo el tiempo específico que deseo saber, en este caso del 1 de enero de 2020 al 30 de junio de 2022. En esta etapa uso la variable plot_rt_es.
df_rt_es.set_index('Date')['Cases'].plot(title='Casos de Covid19 en España desde 20/1/2020 hasta 30/6/2022')
<AxesSubplot:title={'center':'Casos de Covid19 en España desde 20/1/2020 hasta 30/6/2022'}, xlabel='Date'>
url_es = 'https://api.covid19api.com/country/spain/status/confirmed/live'
df_es = pd.read_json(url_es)
df_es
| Country | CountryCode | Province | City | CityCode | Lat | Lon | Cases | Status | Date | |
|---|---|---|---|---|---|---|---|---|---|---|
| 0 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-22 00:00:00+00:00 | |||
| 1 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-23 00:00:00+00:00 | |||
| 2 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-24 00:00:00+00:00 | |||
| 3 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-25 00:00:00+00:00 | |||
| 4 | Spain | ES | 40.46 | -3.75 | 0 | confirmed | 2020-01-26 00:00:00+00:00 | |||
| ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... |
| 893 | Spain | ES | 40.46 | -3.75 | 12818184 | confirmed | 2022-07-03 00:00:00+00:00 | |||
| 894 | Spain | ES | 40.46 | -3.75 | 12818184 | confirmed | 2022-07-04 00:00:00+00:00 | |||
| 895 | Spain | ES | 40.46 | -3.75 | 12890002 | confirmed | 2022-07-05 00:00:00+00:00 | |||
| 896 | Spain | ES | 40.46 | -3.75 | 12890002 | confirmed | 2022-07-06 00:00:00+00:00 | |||
| 897 | Spain | ES | 40.46 | -3.75 | 12890002 | confirmed | 2022-07-07 00:00:00+00:00 |
898 rows × 10 columns
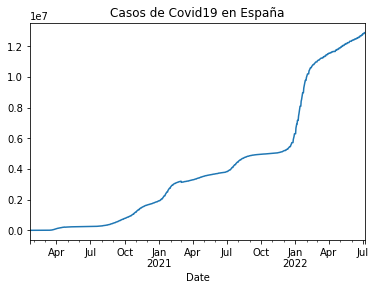
casos_es = df_es.set_index('Date')['Cases']
casos_es.plot(title='Casos de Covid19 en España')
<AxesSubplot:title={'center':'Casos de Covid19 en España'}, xlabel='Date'>
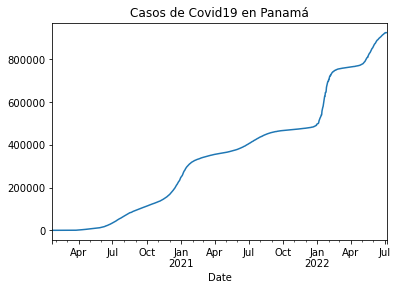
Casos de Covid19 de Panamá
Repetimos el mismo proceso, solo que debemos tener cuidado que los datos sean los de Panamá.
df_es = pd.read_json(url_es)
url_rt_pa = 'https://api.covid19api.com/country/panama/status/confirmed/live'
df_rt_pa = pd.read_json(url_rt_pa)
df_rt_pa
| Country | CountryCode | Province | City | CityCode | Lat | Lon | Cases | Status | Date | |
|---|---|---|---|---|---|---|---|---|---|---|
| 0 | Panama | PA | 8.54 | -80.78 | 0 | confirmed | 2020-01-22 00:00:00+00:00 | |||
| 1 | Panama | PA | 8.54 | -80.78 | 0 | confirmed | 2020-01-23 00:00:00+00:00 | |||
| 2 | Panama | PA | 8.54 | -80.78 | 0 | confirmed | 2020-01-24 00:00:00+00:00 | |||
| 3 | Panama | PA | 8.54 | -80.78 | 0 | confirmed | 2020-01-25 00:00:00+00:00 | |||
| 4 | Panama | PA | 8.54 | -80.78 | 0 | confirmed | 2020-01-26 00:00:00+00:00 | |||
| ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... |
| 894 | Panama | PA | 8.54 | -80.78 | 925254 | confirmed | 2022-07-04 00:00:00+00:00 | |||
| 895 | Panama | PA | 8.54 | -80.78 | 925254 | confirmed | 2022-07-05 00:00:00+00:00 | |||
| 896 | Panama | PA | 8.54 | -80.78 | 925254 | confirmed | 2022-07-06 00:00:00+00:00 | |||
| 897 | Panama | PA | 8.54 | -80.78 | 925254 | confirmed | 2022-07-07 00:00:00+00:00 | |||
| 898 | Panama | PA | 8.54 | -80.78 | 925254 | confirmed | 2022-07-08 00:00:00+00:00 |
899 rows × 10 columns
casos_pa = df_rt_pa.set_index('Date')['Cases']
casos_pa.plot(title='Casos de Covid19 en Panamá')
<AxesSubplot:title={'center':'Casos de Covid19 en Panamá'}, xlabel='Date'>
Ploteamos los países
Es necesario colocar las variables que ya hemos definido para no tener que repetir todo el proceso.
pa_vs_es = pd.concat([casos_es,casos_pa],axis=1)
pa_vs_es
| Cases | Cases | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0.0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0.0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0.0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0.0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0.0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 12818184.0 | 925254 |
| 2022-07-05 00:00:00+00:00 | 12890002.0 | 925254 |
| 2022-07-06 00:00:00+00:00 | 12890002.0 | 925254 |
| 2022-07-07 00:00:00+00:00 | 12890002.0 | 925254 |
| 2022-07-08 00:00:00+00:00 | NaN | 925254 |
899 rows × 2 columns
pa_vs_es.columns = ['España','Panamá']
pa_vs_es
| España | Panamá | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0.0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0.0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0.0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0.0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0.0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 12818184.0 | 925254 |
| 2022-07-05 00:00:00+00:00 | 12890002.0 | 925254 |
| 2022-07-06 00:00:00+00:00 | 12890002.0 | 925254 |
| 2022-07-07 00:00:00+00:00 | 12890002.0 | 925254 |
| 2022-07-08 00:00:00+00:00 | NaN | 925254 |
899 rows × 2 columns
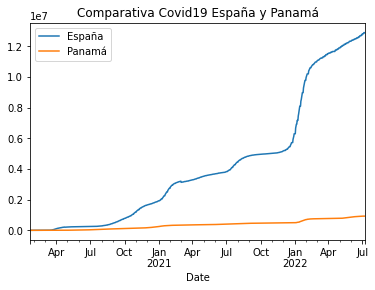
Gráfica comparativa de los casos de Covid19 en España y Panamá
Ya hemos ploteado los indicadores de ambos países, en primera instacia colocando los casos y luego estableciendo el nombre. Con ellos las líneas de cada país se pueden indentificar con mayor facilidad.
pa_vs_es.plot(title='Comparativa Covid19 España y Panamá')
<AxesSubplot:title={'center':'Comparativa Covid19 España y Panamá'}, xlabel='Date'>
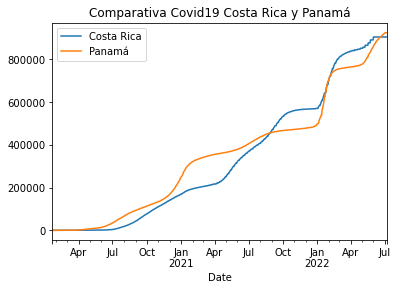
Comparativa de casos entre Costa Rica y Panamá
Repetimos nuevamente los pasos, pero en esta ocasión con Costa Rica, con la finalidad de comparar el comportamiento de la pandemia.
url_rt_cr = 'https://api.covid19api.com/country/costa-rica/status/confirmed/live'
df_rt_cr = pd.read_json(url_rt_cr)
casos_cr = df_rt_cr.set_index('Date')['Cases']
pa_vs_cr = pd.concat([casos_cr,casos_pa],axis=1)
pa_vs_cr
| Cases | Cases | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 904934 | 925254 |
| 2022-07-05 00:00:00+00:00 | 904934 | 925254 |
| 2022-07-06 00:00:00+00:00 | 904934 | 925254 |
| 2022-07-07 00:00:00+00:00 | 904934 | 925254 |
| 2022-07-08 00:00:00+00:00 | 904934 | 925254 |
899 rows × 2 columns
pa_vs_cr.columns = ['Costa Rica','Panamá']
pa_vs_cr
| Costa Rica | Panamá | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 904934 | 925254 |
| 2022-07-05 00:00:00+00:00 | 904934 | 925254 |
| 2022-07-06 00:00:00+00:00 | 904934 | 925254 |
| 2022-07-07 00:00:00+00:00 | 904934 | 925254 |
| 2022-07-08 00:00:00+00:00 | 904934 | 925254 |
899 rows × 2 columns
pa_vs_cr.plot(title='Comparativa Covid19 Costa Rica y Panamá')
<AxesSubplot:title={'center':'Comparativa Covid19 Costa Rica y Panamá'}, xlabel='Date'>
Comparativa con Centroamérica
Los pasos vuelven a ponerse en práctica, pero en esta ocasión con el resto de los países de la región. Es importante cambiar los países para no colocar el de otros y que haya errores.
-Panamá
-Costa Rica
-Nicaragua
-Guatemala
-El Salvador
-Honduras
Gráficas de Panamá vs. el resto de América Central
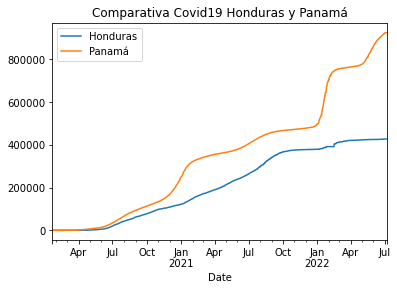
vs. Honduras
url_rt_hon = 'https://api.covid19api.com/country/honduras/status/confirmed/live'
df_rt_hon = pd.read_json(url_rt_hon)
casos_hon = df_rt_hon.set_index('Date')['Cases']
pa_vs_hon = pd.concat([casos_hon,casos_pa],axis=1)
pa_vs_hon
| Cases | Cases | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 427718 | 925254 |
| 2022-07-05 00:00:00+00:00 | 427718 | 925254 |
| 2022-07-06 00:00:00+00:00 | 427718 | 925254 |
| 2022-07-07 00:00:00+00:00 | 427718 | 925254 |
| 2022-07-08 00:00:00+00:00 | 427718 | 925254 |
899 rows × 2 columns
pa_vs_hon.columns = ['Honduras','Panamá']
pa_vs_hon
| Honduras | Panamá | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 427718 | 925254 |
| 2022-07-05 00:00:00+00:00 | 427718 | 925254 |
| 2022-07-06 00:00:00+00:00 | 427718 | 925254 |
| 2022-07-07 00:00:00+00:00 | 427718 | 925254 |
| 2022-07-08 00:00:00+00:00 | 427718 | 925254 |
899 rows × 2 columns
pa_vs_hon.plot(title='Comparativa Covid19 Honduras y Panamá')
<AxesSubplot:title={'center':'Comparativa Covid19 Honduras y Panamá'}, xlabel='Date'>
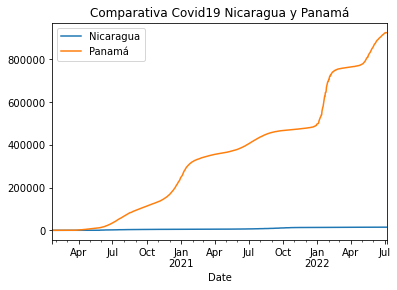
vs. Nicaragua
url_rt_ni = 'https://api.covid19api.com/country/nicaragua/status/confirmed/live'
df_rt_ni = pd.read_json(url_rt_ni)
casos_ni = df_rt_ni.set_index('Date')['Cases']
pa_vs_ni = pd.concat([casos_ni,casos_pa],axis=1)
pa_vs_ni
| Cases | Cases | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 14690 | 925254 |
| 2022-07-05 00:00:00+00:00 | 14690 | 925254 |
| 2022-07-06 00:00:00+00:00 | 14721 | 925254 |
| 2022-07-07 00:00:00+00:00 | 14721 | 925254 |
| 2022-07-08 00:00:00+00:00 | 14721 | 925254 |
899 rows × 2 columns
pa_vs_ni.columns = ['Nicaragua','Panamá']
pa_vs_ni
| Nicaragua | Panamá | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 14690 | 925254 |
| 2022-07-05 00:00:00+00:00 | 14690 | 925254 |
| 2022-07-06 00:00:00+00:00 | 14721 | 925254 |
| 2022-07-07 00:00:00+00:00 | 14721 | 925254 |
| 2022-07-08 00:00:00+00:00 | 14721 | 925254 |
899 rows × 2 columns
pa_vs_ni.plot(title='Comparativa Covid19 Nicaragua y Panamá')
<AxesSubplot:title={'center':'Comparativa Covid19 Nicaragua y Panamá'}, xlabel='Date'>
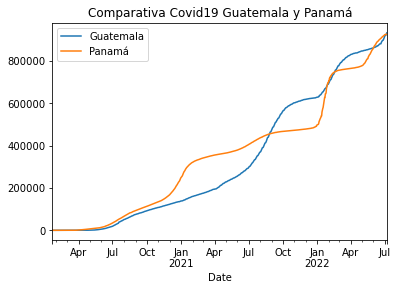
vs. Guatemala
url_rt_gua = 'https://api.covid19api.com/country/guatemala/status/confirmed/live'
df_rt_gua = pd.read_json(url_rt_gua)
casos_gua = df_rt_gua.set_index('Date')['Cases']
pa_vs_gua = pd.concat([casos_gua,casos_pa],axis=1)
pa_vs_gua
| Cases | Cases | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 921146 | 925254 |
| 2022-07-05 00:00:00+00:00 | 922340 | 925254 |
| 2022-07-06 00:00:00+00:00 | 927473 | 925254 |
| 2022-07-07 00:00:00+00:00 | 933259 | 925254 |
| 2022-07-08 00:00:00+00:00 | 933259 | 925254 |
899 rows × 2 columns
pa_vs_gua.columns = ['Guatemala','Panamá']
pa_vs_gua
| Guatemala | Panamá | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 921146 | 925254 |
| 2022-07-05 00:00:00+00:00 | 922340 | 925254 |
| 2022-07-06 00:00:00+00:00 | 927473 | 925254 |
| 2022-07-07 00:00:00+00:00 | 933259 | 925254 |
| 2022-07-08 00:00:00+00:00 | 933259 | 925254 |
899 rows × 2 columns
pa_vs_gua.plot(title='Comparativa Covid19 Guatemala y Panamá')
<AxesSubplot:title={'center':'Comparativa Covid19 Guatemala y Panamá'}, xlabel='Date'>
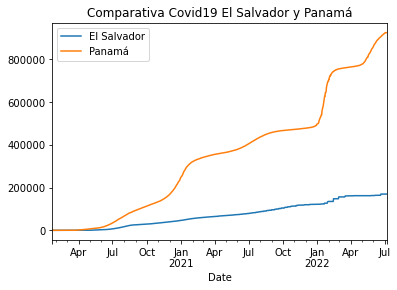
vs. El Salvador
url_rt_sal = 'https://api.covid19api.com/country/el-salvador/status/confirmed/live'
df_rt_sal = pd.read_json(url_rt_sal)
casos_sal = df_rt_sal.set_index('Date')['Cases']
pa_vs_sal = pd.concat([casos_sal,casos_pa],axis=1)
pa_vs_sal
| Cases | Cases | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 169646 | 925254 |
| 2022-07-05 00:00:00+00:00 | 169646 | 925254 |
| 2022-07-06 00:00:00+00:00 | 169646 | 925254 |
| 2022-07-07 00:00:00+00:00 | 169646 | 925254 |
| 2022-07-08 00:00:00+00:00 | 169646 | 925254 |
899 rows × 2 columns
pa_vs_sal.columns = ['El Salvador','Panamá']
pa_vs_sal
| El Salvador | Panamá | |
|---|---|---|
| Date | ||
| 2020-01-22 00:00:00+00:00 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 |
| ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 169646 | 925254 |
| 2022-07-05 00:00:00+00:00 | 169646 | 925254 |
| 2022-07-06 00:00:00+00:00 | 169646 | 925254 |
| 2022-07-07 00:00:00+00:00 | 169646 | 925254 |
| 2022-07-08 00:00:00+00:00 | 169646 | 925254 |
899 rows × 2 columns
pa_vs_sal.plot(title='Comparativa Covid19 El Salvador y Panamá')
<AxesSubplot:title={'center':'Comparativa Covid19 El Salvador y Panamá'}, xlabel='Date'>
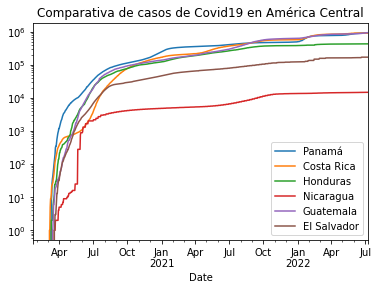
Comportamiento de la Covid19 en Centro América
Adicional a repetir los pasos, al momento de generar la gráfica final es importante agrupar los contenidos con concatenación y darles un nombre sencillo. En este caso ca incluye los seis países.
df_ca = pd.concat([casos_pa,casos_cr,casos_hon,casos_ni,casos_gua,casos_sal],axis=1)
df_ca
| Cases | Cases | Cases | Cases | Cases | Cases | |
|---|---|---|---|---|---|---|
| Date | ||||||
| 2020-01-22 00:00:00+00:00 | 0 | 0 | 0 | 0 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 | 0 | 0 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 | 0 | 0 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 | 0 | 0 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 | 0 | 0 | 0 | 0 |
| ... | ... | ... | ... | ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 925254 | 904934 | 427718 | 14690 | 921146 | 169646 |
| 2022-07-05 00:00:00+00:00 | 925254 | 904934 | 427718 | 14690 | 922340 | 169646 |
| 2022-07-06 00:00:00+00:00 | 925254 | 904934 | 427718 | 14721 | 927473 | 169646 |
| 2022-07-07 00:00:00+00:00 | 925254 | 904934 | 427718 | 14721 | 933259 | 169646 |
| 2022-07-08 00:00:00+00:00 | 925254 | 904934 | 427718 | 14721 | 933259 | 169646 |
899 rows × 6 columns
df_ca.columns = ['Panamá','Costa Rica','Honduras','Nicaragua','Guatemala','El Salvador']
df_ca
| Panamá | Costa Rica | Honduras | Nicaragua | Guatemala | El Salvador | |
|---|---|---|---|---|---|---|
| Date | ||||||
| 2020-01-22 00:00:00+00:00 | 0 | 0 | 0 | 0 | 0 | 0 |
| 2020-01-23 00:00:00+00:00 | 0 | 0 | 0 | 0 | 0 | 0 |
| 2020-01-24 00:00:00+00:00 | 0 | 0 | 0 | 0 | 0 | 0 |
| 2020-01-25 00:00:00+00:00 | 0 | 0 | 0 | 0 | 0 | 0 |
| 2020-01-26 00:00:00+00:00 | 0 | 0 | 0 | 0 | 0 | 0 |
| ... | ... | ... | ... | ... | ... | ... |
| 2022-07-04 00:00:00+00:00 | 925254 | 904934 | 427718 | 14690 | 921146 | 169646 |
| 2022-07-05 00:00:00+00:00 | 925254 | 904934 | 427718 | 14690 | 922340 | 169646 |
| 2022-07-06 00:00:00+00:00 | 925254 | 904934 | 427718 | 14721 | 927473 | 169646 |
| 2022-07-07 00:00:00+00:00 | 925254 | 904934 | 427718 | 14721 | 933259 | 169646 |
| 2022-07-08 00:00:00+00:00 | 925254 | 904934 | 427718 | 14721 | 933259 | 169646 |
899 rows × 6 columns
df_ca.plot(title='Comparativa de casos de Covid19 en América Central',logy=True)
<AxesSubplot:title={'center':'Comparativa de casos de Covid19 en América Central'}, xlabel='Date'>
¿Cómo ha sido el comportamiento de la covid-19 en América Central?
Para entender el comportamiento de la covid19 en Centroamérica hay que tomar en cuenta el factor político. Este es el caso de Nicaragua, cuyas curvas indican que es el país con menos casos en la región. Sin embargo, hay que considerar que su gobierno fue señalado por esconder los casos y también por no brindar los reportes diarios.
Situación contraria ocurre con Costa Rica y Panamá, en los cuales las cifras se han manejado con mayor transparencia a lo largo de toda la pandemia. Con respecto a los números en Panamá, los contagios han aumentado durante el último año debido a la relajación conferida por la vacunación. La tierra del Canal empezó con la inmunización en enero de 2021 y desde entonces las estrictas medidas se flexibilizaron y la población también comenzó reducir las medidas de cuidado.
Entre los meses de mayo y junio, de acuerdo con datos de la Organización Panamericana de la Salud, Centroamérica fue la única subregión que reportó una tendencia a la baja, con una reducción del 32% de los casos de covid-19 y un descenso del 36% de las muertes.
En este último punto, la estrategia de vacunación ha sido importante debido a que desde que se implementó, el número de fallecimientos se ha reducido considerablemente.
No obstante, los encargados de las instituciones sanitarias de la región recuerdan que la pandemia todavía no se ha terminado y es importante continuar con las medidas de bioseguridad.
Cifras de vacunación en América Central por cada 100,000 habitantes
- Costa Rica 209,94
- Panamá 190,77
- Nicaragua 169,21
- El Salvador 167,11
- Honduras 143,14
- Guatemala 109,84